- Биоинформатические подходы к изучению полиморфизмов (SNP): как гены рассказывают свои секреты
- Что такое SNP и почему он так важен для генетики?
- Основные биоинформатические подходы к изучению SNP
- Геномное секвенирование (Next Generation Sequencing, NGS)
- Массивы диагностических ГЕНОМ-микросхем (Genotyping arrays)
- Фаренхитный анализ (Фаренхитное секвенирование)
- Биоинформатические инструменты для анализа данных
- Практическое применение биоинформатических подходов
- Пример исследовательского проекта
- Преимущества и ограничения биоинформатических подходов
- Будущее биоинформатических исследований SNP
- Часто задаваемые вопросы
- Какие SNP самые часто встречающиеся у человека?
- Как биоинформатика помогает выявлять риск заболеваний?
- Топ-10 LSI-запросов по теме и их визуализация
Биоинформатические подходы к изучению полиморфизмов (SNP): как гены рассказывают свои секреты
Современные биоинформатические технологии кардинально меняют наше представление о генетическом разнообразии человека и других организмов. Среди множества методов особое место занимают подходы, связанные с анализом полиморфизмов отдельных нуклеотидов (Single Nucleotide Polymorphisms, или SNP). Эти минимальные изменения в последовательности ДНК могут иметь ключевое значение для понимания генетической предрасположенности к болезням, реакции на лекарства или адаптивных особенностей. В этой статье мы расскажем о том, какие методы используют ученые для выявления и анализа SNP, и как эти знания помогают раскрывать тайны генетической информации.
Что такое SNP и почему он так важен для генетики?
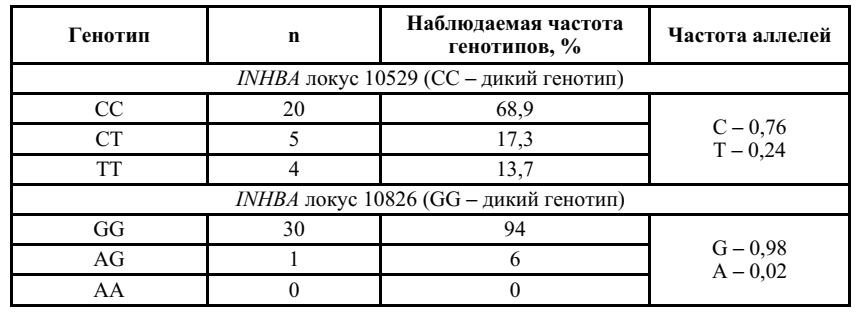
Полиморфизмы отдельного нуклеотида (SNP) — это единичные изменения в последовательности ДНК, которые встречаются у населения с частотой более 1%; Обычно такая замена происходит в одном нуклеотиде: например, вместо тимина (T) у некоторых особей встречается цитозин (C). Несмотря на то, что эти изменения часто нейтральны или не влияют на здоровье, некоторые SNP связаны с риском развития определенных заболеваний или особенностями метаболизма.
Практически все люди имеют миллионы таких вариаций, что делает их уникальными «генетическими отпечатками». Анализ SNP позволяет выявлять ассоциации между генетическими изменениями и клиническими признаками, что открыло путь к персонализированной медицине и более точной диагностике.
Основные биоинформатические подходы к изучению SNP
В современном научном мире существует множество методов и инструментов, которые позволяют выявлять, анализировать и интерпретировать SNP. Рассмотрим наиболее распространенные из них и разберем их принципы:
Геномное секвенирование (Next Generation Sequencing, NGS)
Этот подход позволяет получить огромное количество последовательных данных о ДНК за короткое время и сравнительно низкую стоимость. Современные платформы, такие как Illumina или Ion Torrent, позволяют секвенировать целые геномы или их части, что дает возможность обнаруживать миллионы SNP в одном эксперименте.
Основные этапы:
- Подготовка библиотеки — сегментация и адаптация ДНК;
- Секвенирование — получение длинных последовательностей;
- Обработка данных — выравнивание на референсный геном;
- Обнаружение вариаций — выявление отличий в последовательностях.
Массивы диагностических ГЕНОМ-микросхем (Genotyping arrays)
Этот метод позволяет быстро и относительно дешево определить наличие ряда известных SNP у конкретного человека. Микросхемы содержат множество фиксированных точек-микрообъектов, которые связываются с участками ДНК-образца и показывают наличие вариаций.
Преимущества:
- Быстрый и массовый анализ;
- Высокая точность для известных вариантов;
- Использование при эпидемиологических исследованиях.
Фаренхитный анализ (Фаренхитное секвенирование)
Методика, которая позволяет сосредоточиться на конкретных участках ДНК, известных как кандидатные гены, и сконцентрировать усилия на поиске SNP именно в них, что полезно для изучения связанных с ними признаков.
Биоинформатические инструменты для анализа данных
| Инструмент | Описание | Пример использования | Особенности |
|---|---|---|---|
| GATK | Пакет для обработки данных NGS, поиск вариантов и фильтрация | Обнаружение SNP и INDEL в больших данных | Высокая точность, автоматизация |
| FreeBayes | Модифицированный анализатор вариантов для большего количества данных | Анализ многовалентных вариантов | Удобен для многосемпловых выборок |
| Samtools/BCFtools | Обработка выравниваний и вызов вариантов | Формирование контуров находок SNP | Прост в использовании, надежен |
| PLINK | Статистический анализ генотиповых данных и поиска ассоциаций | GWAS исследования SNP | Мощный анализ больших выборок |
Эти инструменты позволяют автоматизировать работу с большими объемами данных, выявлять вариации и строить статистические модели для определения значимых SNP в рамках исследований.
Практическое применение биоинформатических подходов
Рассмотрим, каким образом эти методы находят свое применение в реальной жизни и научных исследованиях. Среди примеров:
- Изучение наследственных заболеваний: по SNP можно определить предрасположенность к сахарному диабету, онкологическим заболеваниям или сердечно-сосудистым патологиям.
- Персонализированная медицина: подбор лекарственных средств и дозировок основывается на индивидуальных генетических особенностях.
- Эволюционные исследования: анализ вариаций помогает понять, как виды адаптируются к окружающей среде.
- Фармакогеномика: изучение вариаций, влияющих на метаболизм лекарств, улучшает эффективность терапии.
Пример исследовательского проекта
Допустим, мы работаем над изучением генетической предрасположенности к болезни Альцгеймера. Используя геномное секвенирование и анализ SNP, мы выявляем ключевые вариации в генах APOE, CLU и PICALM. Эти данные затем проходят статистическую обработку в ПО типа PLINK для поиска значимых ассоциаций. Полученные результаты позволяют сделать выводы о риске развития заболевания у определенных групп населения;
Преимущества и ограничения биоинформатических подходов
Несмотря на впечатляющие возможности, эти методы не лишены своих недостатков:
- Преимущества:
- Высокая точность и автоматизация анализа;
- Обширные данные о генетическом разнообразии;
- Возможность массового скрининга больших популяций;
- Позволяют выявить даже редкие вариации.
- Не все SNP оказывают клиническое влияние;
- Некоторые методы требуют больших вычислительных ресурсов;
- Контаминанты и ошибки sequencing могут влиять на качество данных;
- Интерпретация результатов — сложный процесс, требующий статистической экспертизы.
Для успешной работы важно учитывать эти нюансы и использовать методики грамотно и системно.
Будущее биоинформатических исследований SNP
Инновации в области секвенирования, развития алгоритмов и вычислительной мощности обещают еще большие достижения. Уже сегодня появляютса новые методы для обнаружения редких вариантов, анализа структурных изменений и интеграции данных из различных источников, эпигенетики, транскриптомики и метаболомики. В дальнейшем можно ожидать более точных моделей предсказания заболеваний и разработки персонализированных методов терапии.
Пределы наших знаний расширяются, а биоинформатика становится ключевым инструментом для раскрытия самых глубоких тайн генетической информации. Это будущее науки, в которое мы все уже вовлечены и часть чего хотели бы стать.
Часто задаваемые вопросы
Какие SNP самые часто встречающиеся у человека?
Наиболее распространенные SNP — это вариации в участках, которые не связаны с болезнями и не имеют значительных последствий. Их можно встретить у подавляющего большинства людей. Такие вариации считаются нейтральными и помогают различать популяции, а также служат базой для изучения генетического разнообразия.
Как биоинформатика помогает выявлять риск заболеваний?
Биоинформатические методы позволяют анализировать огромное количество генетических данных, выявлять ассоциации между SNP и заболеваниями, а также строить модели риска. Благодаря автоматизации и статистическим алгоритмам, мы можем предсказать, насколько вероятно развитие определенных болезней у конкретного человека и выбрать оптимальные стратегии профилактики или лечения.
Топ-10 LSI-запросов по теме и их визуализация
Подробнее
| Genetic variation analysis | Bioinformatics SNP tools | NGS sequencing methods | Genotyping array techniques | SNP disease association studies |
| Computational genomics | Genetic polymorphism analysis | Whole genome sequencing | Variant calling pipelines | Pharmacogenomics SNP analysis |
| GWAS studies and SNP | Data processing in genomics | Genetic markers discovery | Population genetics tools | SNP and health risks |
| Genetic diversity | Bioinformatic pipelines | Rare variants detection | Computational pipelines for SNPs | Personalized medicine genomics |